PUBLICATION
새로 출시된 Sequel II의 early access program에 참여한 연구팀의 사례를 3번에 걸쳐 차례로 소개드립니다.
제 2 편: At Maryland Genomics, Scientists Deploy Sequel II System for a Wide Range of Applications
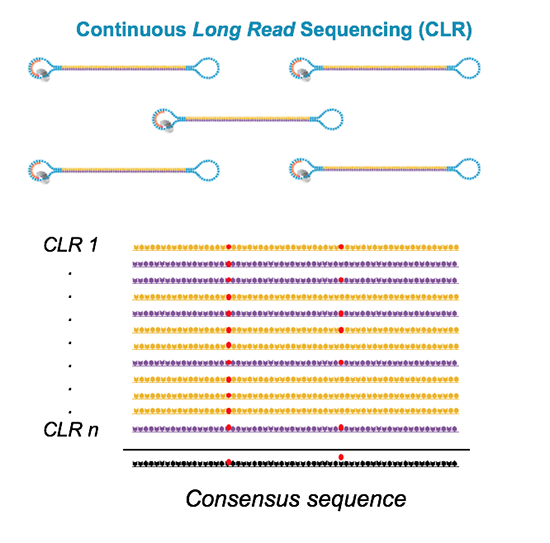
Maryland Genomics 연구팀은 continuous long-read (CLR) sequencing과 circular consensus sequencing을 이용한 HiFi mode 로 다양한 sample type(humans, plants, insects, bacteria, microbiome, and other samples)에 Sequel II system을 적용하였습니다.
CLR (long-read) mode 로 평균 92Gb 의 sequencing data를 생산하였고 HiFi mode에서는 quality score Q32, 평균 260Gb (16Gb이상의 unique molecular yield)를 얻을 수 있었으며 이는 기존 모델인 Sequel system의 10배 이상의 생산성 증가라고 설명하고 있습니다.
연구팀이 Seqeul II에 적용한 application은 다음과 같습니다.
16 plex microbial pool(80Mb)의 sequencing
- 하나의 SMRT cell 8M으로 215Gb data를 생산하여 high-quality assembly를 생성 (99.9% completeness)
- 16개 중 12개의 chromosome은 single contig으로 어셈블리 완성
Full-length 16S amplicon sequencing using HiFi mode
- Mock communities와 infant gut sample로 구성된 96-plex 16S amplicon library를 HiFi mode로 sequencing
- 3’end degradation 없고, Q80의 quality score를 가진 data 생산
- 샘플당 12000개의 HiFi read를 얻었으며 그중 87%는 종(species) 수준- 일부는 아종(sub-species)의 분류에 적용
Metagenome shotgun sequencing
- starting 양이 부족하고 host contamination이 높은 조건의 vaginal microbiome samples에서 complete genome assemble을 목표로 진행
- 샘플에 포함되어 있는 배양이 어렵고 Reference genome이 없는 BVAB1 (Bacterial Vaginosis Associated Bacteria 1)의 draft genome 생성
더 자세한 내용은 아래의 동영상에서 확인하실 수 있습니다.










